几种国内芯片测序格式和 Affymetrix 位点集格式的对比
前3篇文章都是对比和 Illumina 芯片有关的原始数据格式,这篇则直接比较和 Affymetrix 芯片有关的原始数据格式。目前国内常见的测序机构里,23魔方主要使用与 Affymetrix 有关的定制芯片,据说新版也用了 Illumina 定制芯片,但真实性未知。而其他测序公司比如微基因、各色等,基本都使用或者改用 Illumina 的芯片(微基因的1.0版用 Affymetrix 的定制芯
前3篇文章都是对比和 Illumina 芯片有关的原始数据格式,这篇则直接比较和 Affymetrix 芯片有关的原始数据格式。
目前国内常见的测序机构里,23魔方主要使用与 Affymetrix 有关的赛默飞世尔定制芯片,据说新版也用了 Illumina 定制芯片,但真实性未知。而其他测序公司比如微基因、各色等,基本都使用或者改用 Illumina 的芯片(微基因的1.0版用 Affymetrix 的定制芯片)。
而国外常见的5家(23andMe、Ancestry、FTDNA、LivingDNA、MyHeritage)测序机构里,LivingDNA 的 V2 版本改用了 Affymetrix 的定制芯片。且 FTDNA 最早期的 hg18 (NCBI36) 坐标版本格式也是 Affymetrix 的,但很快就变更为 Illumina Omni 系列的定制芯片。
而 Affymetrix 的常用官方芯片数据种类不如 Illumina 格式丰富,因此下述的对比图只选取了较有用的几种类型。
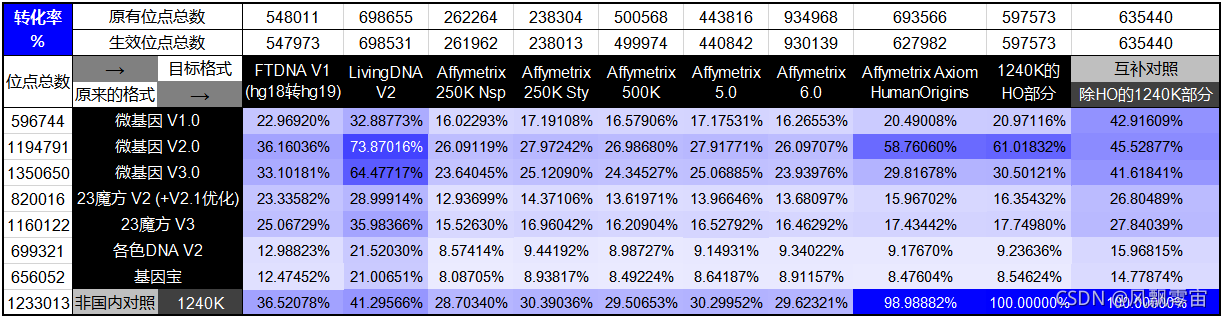
1.国内格式转国外与 Affymetrix 相关格式的转化率图(按基因位点位置转化)
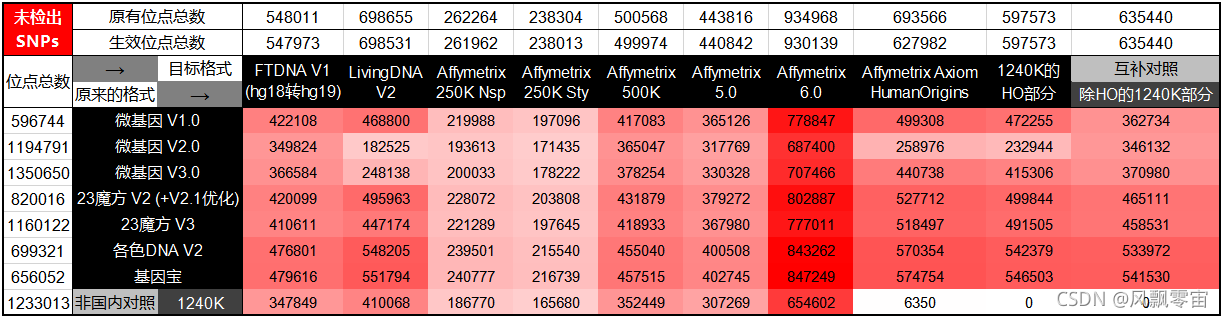
2.国内格式转国外与 Affymetrix 相关格式的未检出位点数图
3.上述格式跑一些祖源计算器的理想利用率图(这里的原始数据文件第4列都填满了纯合位点,其中“[#ANY]”代表这个系列下的任意一个计算器)
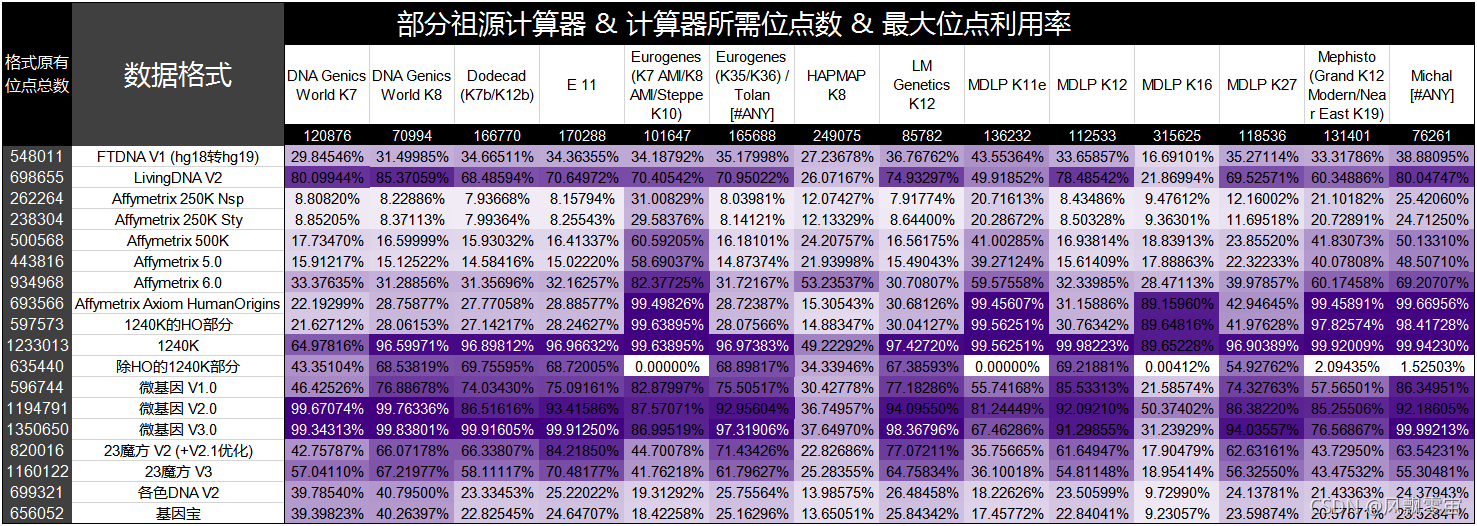
为了方便对比,这次我对 1240K 科研样本格式作了分解,分为 HO(Human Origins,人类起源,部分科研样本是这种格式而非1240K) 部分和非 HO 部分,而且这里用到的 Affymetrix Axiom HumanOrigins 格式位点名以“rs”开头为主,未以大量“Affx-”开头位点为主(在 Axiom 系列格式里,绝大多数基因位点有3种命名方式,少数仅有2种),因此第三幅图中的统计还没达到跑 MDLP K16 这个同时计算“rs”、“Affx-”开头位点计算器的最大位点利用率。
从整体来看,国内格式转化到 Affymetrix 格式的转化率都不理想,仅微基因2.0版对 Affymetrix Human Origins 位点集相对兼容些(同时微基因2.0也更兼容 Illlumina GSA 位点集)。如果您需要用到自己数据的 Affymetrix 官方格式,本人建议使用从全基因组数据的 BAM 或 CRAM 文件提取到芯片格式的方法。

魔乐社区(Modelers.cn) 是一个中立、公益的人工智能社区,提供人工智能工具、模型、数据的托管、展示与应用协同服务,为人工智能开发及爱好者搭建开放的学习交流平台。社区通过理事会方式运作,由全产业链共同建设、共同运营、共同享有,推动国产AI生态繁荣发展。
更多推荐
 已为社区贡献1条内容
已为社区贡献1条内容







所有评论(0)