大数据深度学习|计算机毕设项目|计算机毕设答辩|Flask--基于Transformer的医学图像分割
本文研究了基于Transformer的医学图像分割技术,重点对比分析了TransUNet和MobileViT两种模型在脑肿瘤、皮肤病变和肺结节分割任务中的表现。实验结果表明,TransUNet在Dice系数(0.7588)、IoU(0.6113)等指标上略优于MobileViT,但后者在计算效率方面更具优势。研究采用Flask框架构建Web应用,实现了医学图像上传、处理和可视化功能。未来工作将聚焦

标题:Flask--基于Transformer的医学图像分割
文档介绍:
医学图像分割是医学影像分析中的关键技术,其在疾病诊断、治疗方案制定等方面发挥着至关重要的作用。通过精确的图像分割,医生能够更清晰地观察到病变区域,准确判断病情,从而制定出更加个性化的治疗方案。这不仅提高了诊断的准确性,也为患者提供了更好的治疗效果,极大地推动了医学的发展。
近年来,基于Transformer的医学图像分割技术逐渐兴起。Transformer技术最初在自然语言处理领域取得了巨大成功,其强大的特征提取和长距离依赖建模能力使其在医学图像分割领域也展现出巨大潜力。相较于传统的卷积神经网络(CNN)方法,Transformer能够更好地捕捉图像中的全局信息,有效避免了CNN在处理长距离依赖时的局限性。此外,Transformer的并行计算特性也使其在训练效率上具有明显优势,进一步提升了医学图像分割的性能。
在构建医学图像分割Web应用方面,Flask框架具有独特的价值。Flask作为轻量级的Web应用框架,以其简洁、灵活和高效的特点,为开发者提供了便捷的开发环境。通过Flask,开发者可以快速搭建出功能强大的Web应用,实现医学图像的上传、处理、分割和结果展示等功能。同时,Flask的模块化设计使得系统具有良好的可扩展性,便于后续的功能升级和维护。借助Flask框架,医学图像分割技术能够更广泛地应用于临床实践,为医生和患者提供更加便捷、高效的医疗服务。
综上所述,基于Transformer的医学图像分割技术凭借其卓越的性能和Flask框架的便捷性,具有重要的研究背景和意义。这一技术的深入研究与应用,将有力推动医学影像分析领域的发展,为疾病诊断和治疗提供更加精准、高效的技术支持。
在国内,随着深度学习技术的迅猛发展,Transformer 模型在自然语言处理领域取得了显著成果,其强大的特征提取和自注意力机制逐渐被引入到医学图像分割领域。国内研究者在这一领域进行了大量探索,取得了一系列创新性成果。由慕尼黑工业大学、复旦大学和华为的研究者田奇等人在 2024 年 7 月 26日提出的 Swin-Unet,是首个基于纯Transformer 的 U-Net 形医学图像分割网络。该网络利用 Swin Transformer 的层次化结构和局部注意力机制,有效提升了医学图像分割的精度和效率。Swin-Unet 在多个公开数据集上展示了优异的性能,为医学图像分割领域带来了新的突破。北京信息科技大学的王茜等人提出了一种名为 ParaCNNFormer 的混合架构分割模型。该模型结合了卷积神经网络(CNN)和 Swin Transformer 的优点,利用 CNN 提取局部细节特征,同时利用 Swin Transformer 建立长距离依赖关系,有效提高了分割准确度。针对医学图像的噪声、伪影以及边界不清晰等问题,提出了一种基于 UNet 架构的双解码器医学图像分割算法 DDS-UNet。该算法在下采样过程中通过层级式 Swin Transformer 提取不同尺度目标的关键信息,并在上采样过程中利用 Swin Transformer和 CNN 的双解码器从不同角度聚合多尺度语义信息,逐级恢复医学图像空间信息。国内研究者不仅关注新模型的构建,还致力于现有模型的优化和性能提升。通过设计更高效的注意力机制、减少模型参数量、提高计算效率等方式,研究者们不断推动基于 Transformer 的医学图像分割技术向更高水平发展。例如,一些研究团队通过改进 Transformer 的编码器和解码器结构,实现了更精细的图像特征提取和更准确的分割结果。国内研究者还积极探索基于 Transformer 的多模态医学图像分割技术。通过融合不同模态的医学图像信息,如 CT、MRI 等,研究者们构建了更全面、更准确的医学图像分割模型。这些多模态模型在复杂医学场景下展现了更强的适应性和鲁棒性。
在国外,基于 Transformer 的医学图像分割研究同样如火如荼,众多顶尖研究机构和团队在这一领域取得了显著成果。由约翰霍普金斯大学、电子科技大学、斯坦福大学等机构的研究者在 2021 年提出的 TransUNet,该模型结合了 Tr
ansformers 和 U-Net 的优点,用于医学图像分割。TransUNet 利用 Transformer的强大特征提取能力,结合 U-Net 的编码器-解码器结构,实现了更准确、更高效的医学图像分割。该模型在多个公开数据集上展示了卓越的性能,成为医学图像分割领域的经典之作。由美国佛罗里达理工学院的三位学生于 2023 年 11月 10 日提出的 seUNet,是一种简单而有效的医学图像分割 UNet-Transformer模型。该模型通过将 Transformer 模块嵌入到 U-Net 结构中,实现了对医学图像的精细分割。seUNet 在保持模型简洁性的同时,取得了与复杂模型相媲美的性能,为医学图像分割领域提供了新的思路。由 Shehan Perera 等人于 2024 年在CVPR 会议上提出的 SegFormer3D,是一种高效的 3D 医学图像分割 Transformer。该模型利用三维卷积和自注意力机制,实现了对三维医学图像的快速、准确分割。SegFormer3D 在多个三维医学图像数据集上取得了优异的性能,为三维医学图像分割领域提供了新的解决方案。
基于 Transformer 的医学图像分割技术在国内外均取得了显著进展,展示了其在高精度和高效处理医学图像方面的巨大潜力。未来,随着研究的深入和技术的不断发展,我们期待看到更多创新性的模型和算法涌现,为医学图像分割领域带来更多突破和进步。同时,国内外研究者的合作与交流也将进一步推动这一领域的发展,为医学诊断和治疗提供更大的技术支持。
研究内容主要围绕深入理解Transformer的结构特点、在医学图像数据集上实现基于Transformer的图像分割模型,以及对所设计算法进行全面测试和评估展开。首先,将深入分析Transformer的结构特点,包括自注意力机制、多头注意力、位置编码等关键组件,以理解其在序列数据处理中的优势,这些优势使其能够捕捉图像中的长距离依赖关系和全局信息,为医学图像分割提供新的视角和方法。其次,选择合适的医学图像数据集,如MRI、CT等,利用深度学习框架如TensorFlow或PyTorch实现所设计的基于Transformer的医学图像分割模型。在实验过程中,将进行模型的训练、验证和测试,详细记录实验过程和结果,以评估模型在医学图像分割任务上的性能。最后,对设计实现的医学图像分割软件算法进行全面的测试和评估,确保其在实际应用中的稳定性和可靠性。同时,撰写详细的设计文档,记录算法的设计思路、实现方法和使用说明,以便于其他研究人员和开发者理解和应用该算法。通过这些研究内容,旨在推动基于Transformer的医学图像分割技术的发展,为医学影像分析提供更加强大的工具和方法。
设计方案:
- 广泛阅读相关领域的文献,学习基于Transformer的医学图像分割算法,选择两种算法进行实现;
2. 在数据集上运行TransUNet、MobileViT算法,对算法模型进行评估并测试;
3. 使用 Matplotlib 或 OpenCV 显示原始图像与分割结果。
1.知识学习:完成对python语言、数字图像处理、深度学习相关领域的学习,熟悉基于Transformer的分割算法;Transformer架构如图1所示。
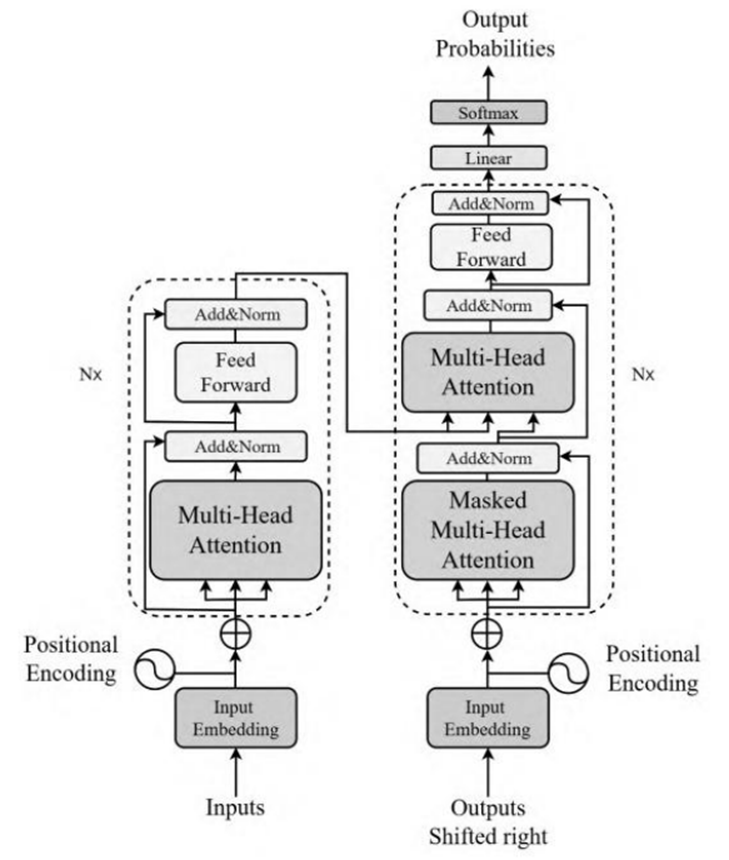
图1-1 Transformer总体框架
2.数据集收集:收集课题中所需要的数据集,如BraTs:脑肿瘤分割挑战数据集;ISBI Skin Lesion:皮肤病变分割数据集;LUNA16:肺结节检测数据集;
3.算法设计:使用 Python 实现 TransUNet、MobileViT 算法,TransUNet 结合了 Transformer 和 U-Net 的优势,适用于多种医学图像分割任务。适用于多器官分割,病毒检测等。MobileViT 是一种轻量级 Transformer 模型,专为移动和边缘设备设计。适应于实时性要求较高的应用,如移动健康监测;
4.评估并优化算法:评估算法的准确率(Accuracy,ACC)、Dice 系数(Dicecoefficient)、特异性(Specificity,SPE)、灵敏度(Sensitivity,SEN)、精确度(Precision)、召回率(Recall)等性能指标并进行优化。实现的算法在公开数据集上应有较高的分割准确率。
- 2 章 相关技术与理论基础
- Transformer原理与在医学图像分割中的应用
- Transformer基本架构与自注意力机制
- Transformer原理与在医学图像分割中的应用
Transformer原理与在医学图像分割中的应用中,Transformer的基本架构和自注意力机制是核心要素。Transformer模型是一种基于自注意力机制的深度神经网络模型,经常用于处理序列数据。它的核心思想是通过自注意力机制来捕捉序列内部的长距离依赖关系,从而更好地理解和生成序列数据。
在医学图像分割中,Transformer的应用主要体现在其能够有效地捕捉图像中的全局信息,并且对图像的局部细节有很好的建模能力。自注意力机制通过计算序列中各个位置之间的注意力权重,来决定每个位置对其他位置的依赖程度。这种机制使得Transformer模型能够动态地关注序列中的关键信息,而忽略不重要的信息。
在医学图像分割任务中,自注意力机制可以帮助模型更好地理解图像中的病变区域和正常组织的边界。通过计算图像中各个像素点之间的注意力权重,模型可以更加精确地分割出病变区域,从而为医生提供更准确的诊断依据。
此外,Transformer的另一个重要组成部分是多头注意力机制。多头注意力机制通过将输入序列分割成多个头,每个头关注不同的信息,然后将这些头的输出拼接起来,以获得更丰富的表示。在医学图像分割中,多头注意力机制可以帮助模型同时关注图像中的多个特征,从而提高分割的准确性。
最后,位置编码是Transformer中的另一个关键组件。由于自注意力机制本身并不考虑序列中位置的信息,因此需要引入位置编码来保留序列中位置的信息。在医学图像分割中,位置编码可以帮助模型更好地理解图像中的空间结构,从而提高分割的准确性。
综上所述,Transformer的基本架构和自注意力机制在医学图像分割中具有重要的应用价值。通过自注意力机制,模型可以更好地捕捉图像中的全局信息和局部细节;通过多头注意力机制,模型可以同时关注图像中的多个特征;通过位置编码,模型可以更好地理解图像中的空间结构。这些特性使得Transformer模型在医学图像分割任务中具有很大的潜力。
-
-
- 基于Transformer的医学图像分割模型的发展历程
-
基于Transformer的医学图像分割模型的发展历程是一个从初步探索到逐渐成熟的过程。最初,Transformer模型主要应用于自然语言处理领域,如机器翻译和文本生成等任务。随着研究的深入,研究人员开始探索将Transformer应用于计算机视觉领域,特别是医学图像分割任务。
在医学图像分割中,Transformer的应用最初面临着一些挑战。医学图像通常具有高分辨率和复杂的结构,这使得传统的Transformer模型难以直接应用于医学图像分割任务。为了克服这些挑战,研究人员提出了一系列改进的Transformer模型,如ViT(Vision Transformer)、Swin Transformer等。这些模型通过引入图像特定的操作和结构,使得Transformer能够更好地处理医学图像数据。
随着基于Transformer的医学图像分割模型的不断发展,其在医学影像分析中的应用也越来越广泛。例如,在肺癌筛查中,基于Transformer的模型可以自动分割出肺结节区域,帮助医生更准确地诊断肺癌。在脑部疾病诊断中,Transformer模型可以分割出脑部病变区域,为医生提供更准确的诊断依据。
此外,基于Transformer的医学图像分割模型还具有很强的可扩展性和灵活性。研究人员可以根据不同的医学图像分割任务,设计不同的Transformer模型结构,以满足不同的需求。同时,基于Transformer的模型还可以与其他深度学习模型相结合,如卷积神经网络(CNN)等,以进一步提高分割的准确性。
总之,基于Transformer的医学图像分割模型的发展历程是一个不断创新和发展的过程。从最初的初步探索到逐渐成熟,Transformer模型在医学图像分割中的应用越来越广泛,为医学影像分析提供了强大的工具和方法。随着研究的不断深入,相信基于Transformer的医学图像分割模型将会在医学领域发挥越来越重要的作用。
TransUNet模型的网络结构巧妙地融合了U-Net的U型编解码架构和Transformer的自注意力机制,旨在提升医学图像分割的性能。该模型主要由三个部分组成:编码器(Encoder)、Transformer编码器(Transformer Encoder)和解码器(Decoder)。
在编码器部分,TransUNet采用了与U-Net类似的卷积层和池化层来逐步降低特征图的空间分辨率,同时增加特征图的通道数,以提取图像的多尺度特征。这一部分与传统的U-Net编码器结构基本相同,通过卷积操作提取局部特征,并通过下采样操作减少计算量,同时增加特征的抽象程度。
紧接着编码器之后,TransUNet引入了Transformer编码器部分,这是该模型的核心创新点。这一部分利用Transformer的自注意力机制来捕捉特征图中的全局依赖关系。具体来说,Transformer编码器将编码器输出的多尺度特征图转换为序列形式,然后通过自注意力机制计算不同位置特征之间的相关性,从而捕捉长距离的依赖关系。多头注意力机制进一步允许模型同时关注多个特征子空间,增强了对图像全局信息的理解。位置编码则用于保留特征图中的空间信息,确保模型能够理解特征图的空间结构。
在解码器部分,TransUNet采用了与U-Net类似的反卷积层(也称为转置卷积层)和跳层连接(Skip Connection)来逐步恢复特征图的空间分辨率。解码器将Transformer编码器输出的全局特征与编码器中对应尺度的特征图进行融合,通过跳层连接将编码器中提取的局部特征与Transformer编码器中学习的全局特征相结合,从而在解码过程中同时利用局部和全局信息。最终,解码器输出与输入图像相同分辨率的分割结果图。
总的来说,TransUNet的网络结构通过结合U-Net的U型编解码架构和Transformer的自注意力机制,有效地结合了局部特征提取和全局信息捕捉的能力,使其在医学图像分割任务中能够取得更出色的性能。
TransUNet模型在医学图像分割中展现出显著的优势,这些优势主要源于其独特的网络结构和对Transformer技术的巧妙应用。首先,TransUNet通过引入Transformer编码器,显著增强了模型捕捉全局信息的能力。在医学图像分割中,全局信息的捕捉对于准确分割和理解图像至关重要,因为医学图像往往包含复杂的解剖结构和病变区域,这些区域可能跨越较大的空间范围。传统的卷积神经网络(CNN)在处理这类图像时,由于卷积操作的局部性,可能难以捕捉到长距离的依赖关系。而Transformer的自注意力机制能够有效地建模不同位置特征之间的全局依赖关系,从而更准确地捕捉到病变区域的全局特征,提高分割的准确性。
其次,TransUNet结合了U-Net的U型编解码架构,这一设计使得模型能够同时利用局部和全局信息。U-Net架构通过编码器逐步提取图像的多尺度特征,并通过解码器逐步恢复特征图的空间分辨率。在解码过程中,通过跳层连接将编码器中提取的局部特征与Transformer编码器中学习的全局特征相结合,使得模型能够在分割过程中同时考虑到局部细节和全局结构。这种结合使得TransUNet在处理复杂的医学图像时,能够更准确地分割出病变区域,同时保留更多的细节信息。
此外,TransUNet的多头注意力机制进一步增强了模型对图像特征的理解能力。多头注意力机制允许模型同时关注多个特征子空间,从而更全面地捕捉图像的特征信息。在医学图像分割中,这种多角度的特征捕捉能力有助于模型更准确地识别和理解不同类型的病变区域,提高分割的鲁棒性。
最后,TransUNet在训练和推理过程中表现出较高的效率和较好的泛化能力。尽管Transformer的计算复杂度较高,但通过巧妙的设计和优化,TransUNet在保持高性能的同时,仍然能够保持较高的推理速度。这使得TransUNet在实际应用中具有较好的实用性,能够满足医学图像分割任务对实时性和准确性的要求。
综上所述,TransUNet模型通过引入Transformer编码器、结合U-Net的U型编解码架构、应用多头注意力机制以及优化训练和推理过程,在医学图像分割中展现出显著的优势。这些优势使得TransUNet在处理复杂的医学图像时,能够更准确地分割出病变区域,同时保留更多的细节信息,提高了分割的准确性和鲁棒性,具有重要的研究和应用价值。
MobileViT模型是一种轻量级的视觉Transformer模型,其网络结构与特点使其在移动设备和资源受限的环境中表现出色。MobileViT的设计目标是结合Transformer的强大特征提取能力与移动设备的计算和存储限制,通过精心设计的网络结构实现高效的性能。
MobileViT的网络结构主要由三个部分组成:局部表示学习、全局表示学习和轻量级Transformer块。首先,局部表示学习部分采用传统的卷积神经网络(CNN)层,负责提取输入图像的局部特征。这一部分利用CNN的局部感知能力,快速捕捉图像的细节信息,为后续的Transformer块提供基础特征。
接着,全局表示学习部分引入了轻量级的Transformer块,这是MobileViT的核心特点之一。与传统的Transformer模型相比,MobileViT中的Transformer块采用了局部注意力机制,以减少计算复杂度和参数数量。通过将输入特征图划分为多个非重叠的局部区域,并在每个区域内独立计算自注意力,MobileViT能够有效地捕捉全局依赖关系,同时降低计算成本。这种局部注意力机制使得MobileViT在保持Transformer强大特征提取能力的同时,显著减少了计算资源的需求。
此外,MobileViT还采用了级联的卷积层和Transformer块的混合结构,进一步优化了模型的性能。在每个Transformer块之后,模型使用卷积层对特征图进行下采样,以减少特征图的空间尺寸,同时增加通道数。这种设计不仅有助于降低计算复杂度,还使得模型能够更好地处理不同尺度的特征,提高对复杂图像的理解能力。
MobileViT的另一个重要特点是其轻量级的网络设计。通过采用深度可分离卷积、通道shuffle等轻量级操作,MobileViT在保持高性能的同时,显著减少了模型的参数数量和计算量。这使得MobileViT在移动设备和资源受限的环境中具有更高的实用性和可部署性。
综上所述,MobileViT模型通过结合局部表示学习和全局表示学习,采用轻量级的Transformer块和级联的卷积层,以及轻量级的网络设计,实现了在移动设备上的高效性能。其网络结构与特点使其在图像分类、目标检测等视觉任务中表现出色,具有重要的研究和应用价值。
MobileViT模型在医学图像分割中展现出显著的优势,主要源于其轻量级设计、高效的特征提取能力以及对全局上下文信息的有效捕捉。这些优势使得MobileViT在处理医学图像时能够提供更准确、更快速的分割结果,从而在临床诊断和治疗规划中发挥重要作用。
首先,MobileViT的轻量级设计使其非常适合在计算资源有限的医疗设备上部署。医学图像分割通常需要处理大量的数据,并且对实时性有较高要求。MobileViT通过采用深度可分离卷积和局部注意力机制,显著减少了模型的参数数量和计算量,使其能够在不牺牲性能的情况下,快速处理医学图像。这种轻量级特性使得MobileViT可以在移动设备、嵌入式系统等资源受限的环境中高效运行,为医疗影像分析提供了更多的应用场景。
其次,MobileViT在特征提取方面的优势使其在医学图像分割中表现出色。医学图像通常包含复杂的结构和细微的细节,需要模型具备强大的特征提取能力。MobileViT通过结合卷积神经网络和Transformer的优势,能够同时捕捉局部细节和全局上下文信息。卷积层负责提取图像的局部特征,而Transformer块则通过自注意力机制捕捉全局依赖关系,这种混合结构使得MobileViT能够更全面地理解医学图像的内容,从而提高分割的准确性。
此外,MobileViT的局部注意力机制在医学图像分割中尤为重要。医学图像中的病变区域往往具有特定的形状和纹理特征,这些特征在不同尺度上可能表现出不同的模式。MobileViT通过将输入特征图划分为多个局部区域,并在每个区域内独立计算自注意力,能够有效地捕捉这些多尺度特征。这种局部注意力机制不仅减少了计算复杂度,还使得模型能够更好地关注病变区域的细节,提高分割的精度。
最后,MobileViT的灵活性和可扩展性使其在医学图像分割中具有广泛的应用前景。通过调整网络结构中的参数,MobileViT可以适应不同类型的医学图像和分割任务。例如,对于高分辨率的医学图像,可以通过增加Transformer块的数量和深度来提高模型的性能;而对于实时性要求较高的应用场景,可以通过减少参数数量和计算量来优化模型的运行速度。这种灵活性使得MobileViT能够满足不同医学图像分割任务的需求,为临床诊断和治疗提供有力的技术支持。
综上所述,MobileViT模型在医学图像分割中的优势主要体现在其轻量级设计、高效的特征提取能力、局部注意力机制以及对不同任务的适应性。这些优势使得MobileViT在处理医学图像时能够提供更准确、更快速的分割结果,具有重要的研究和应用价值。
-
- Flask框架介绍
Flask是一个轻量级Web应用框架。它的核心构成有路由系统、请求处理机制、模板引擎以及插件扩展机制。路由系统借助装饰器,让开发者可以便捷地设定URL与处理函数的对应关系。在请求处理过程中,Flask会自动剖析客户端发起的各类请求,不管是常规的GET、POST请求,还是带有复杂参数的请求,它都能正确地处理,并将最后结果打包成响应反还给客户端。
在模板引擎层面,开发者能够将Python的代码插入到HTML模板中,生成动态网页内容从而达成数据与页面展示的分离,这样做可以提升代码的可读性与可维护性。Flask还具备丰富的插件扩展机制,例如Flask - SQLAlchemy、Flask - Login等。借助这些插件,开发者能够迅速为应用增添各类功能。无论是搭建小型个人项目,还是参与大型企业级Web应用部分模块的开发,Flask都可以充分发挥自身特性,给开发工具充当加油站,满足多样化的开发需求。
在医学图像分割的研究中,选择和使用高质量的数据集是确保模型训练效果和泛化能力的关键。为了满足不同医学图像分割任务的需求,研究者通常会收集和整理多种类型的医学图像数据集。以下是几个在医学图像分割领域常用的数据集介绍:
BraTS(Brain Tumor Segmentation)数据集:BraTS数据集是一个专门用于脑肿瘤分割的挑战数据集,由多个医学中心合作收集和整理。该数据集包含了多模态的脑部磁共振成像(MRI)图像,包括T1、T1ce、T2和FLAIR等序列。每个样本都由专家进行了详细的标注,包括肿瘤核心、水肿和坏死组织等区域。BraTS数据集的多样性和复杂性使其成为评估脑肿瘤分割算法性能的重要基准。
ISBI Skin Lesion数据集:ISBI Skin Lesion数据集是一个用于皮肤病变分割的数据集,由国际皮肤影像学学会(ISBI)提供。该数据集包含了大量的皮肤病变图像,包括良性和恶性肿瘤,以及多种类型的皮肤病变。每个样本都由专家进行了标注,提供了病变区域的精确轮廓。ISBI Skin Lesion数据集的多样性和高质量标注使其成为皮肤病变分割任务的重要资源。
LUNA16数据集:LUNA16数据集是一个用于肺结节检测的数据集,由Lung Nodule Analysis 2016挑战赛提供。该数据集包含了大量的肺部CT扫描图像,由多名放射科医生进行了标注,提供了肺结节的位置、大小和恶性概率等信息。LUNA16数据集的多样性和标注质量使其成为肺结节检测和分割任务的首选数据集之一。
这些数据集的收集和整理通常涉及多个医学中心和专家的合作,以确保数据的多样性和标注质量。在使用这些数据集时,研究者需要遵守相关的伦理和隐私保护规定,确保数据的合法使用。通过这些高质量的数据集,研究者可以开发和验证各种医学图像分割算法,推动医学影像分析技术的发展。
数据预处理是医学图像分割任务中不可或缺的一环,它对于提高模型训练的效率和准确性具有至关重要的作用。在处理BraTS、ISBI Skin Lesion和LUNA16等数据集时,数据预处理主要包括以下几个方面:
数据清洗:首先,需要对原始数据进行清洗,去除图像中的噪声和伪影。对于MRI图像,可能需要使用滤波器来减少磁场不均匀性和运动伪影的影响。对于CT图像,可能需要校正由于患者呼吸或心脏搏动引起的伪影。
数据归一化:为了消除不同图像间强度差异的影响,需要对图像进行归一化处理。这通常包括将图像强度值缩放到一个固定的范围,如[0, 1]或[-1, 1]。归一化有助于加快模型训练的收敛速度,并提高模型的泛化能力。
数据增强:为了增加模型的鲁棒性和泛化能力,通常需要对数据进行增强。这包括对图像进行旋转、缩放、翻转、裁剪等操作。对于医学图像,还需要考虑保持病变区域的解剖结构不变,以确保增强后的图像仍然具有临床意义。
数据标注:对于分割任务,需要为每个图像提供精确的标注。这通常由医学专家手动完成,或者使用半自动标注工具辅助完成。标注工作需要确保病变区域的边界清晰,以便模型能够学习到准确的分割边界。
数据划分:在训练模型之前,需要将数据集划分为训练集、验证集和测试集。这有助于评估模型的性能,并防止模型在训练过程中过拟合。通常,训练集占总数据集的70%-80%,验证集占10%-15%,测试集占10%-15%。
数据加载和批处理:在训练过程中,需要高效地加载数据并进行批处理。这通常使用Python中的NumPy库或TensorFlow和PyTorch等深度学习框架中的数据加载器实现。通过批处理,可以减少内存消耗,并提高模型的训练速度。
通过以上数据预处理步骤,可以确保医学图像分割任务中的数据质量,提高模型的训练效率和准确性。这对于推动医学影像分析技术的发展具有重要意义。
在构建基于Transformer的医学图像分割Flask应用时,环境配置是一个重要的环节,它直接影响到开发的效率、应用的性能以及最终的运行效果。以下是针对您提供的硬件和软件环境,进行基于Transformer的医学图像分割应用开发的一些建议和配置说明:
硬件环境:
处理器:Intel(R) Core(TM) i7-10750H CPU @ 2.60GHz。这款处理器拥有6核心12线程,主频2.6GHz,最高可达5.0GHz的Turbo Boost速度,能够提供强大的计算能力,对于运行深度学习模型和Flask应用来说非常合适。
内存:16GB 3200 MHz DDR4。这样的内存配置可以支持较大规模的数据处理和模型训练,同时也能保证Flask应用在处理并发请求时的稳定性。
显卡:NVIDIA GeForce GTX 1660 Ti。这款显卡拥有1536个CUDA核心,基础频率为1150MHz,Boost频率可达1200MHz,配备6GB GDDR6显存,能够加速深度学习模型的训练和推理过程,特别是对于Transformer这类计算密集型的模型。
软件环境:
操作系统:Windows11 家庭中文版。Windows11提供了良好的用户界面和系统稳定性,同时也支持大部分的开发工具和库。在Windows11上,您可以通过Windows Subsystem for Linux (WSL)来安装Linux发行版,以便更好地支持Python开发环境和深度学习框架。
Python环境:建议使用Python 3.8或更新的版本,因为它提供了更好的性能和库支持。您可以通过Anaconda或Miniconda来创建一个虚拟环境,以便于管理和隔离项目依赖。
Flask框架:Flask是一个轻量级的Web框架,用于构建Web应用。您可以通过pip安装Flask及其相关扩展,如Flask-RESTful用于构建RESTful API。
其他依赖库:您可能还需要安装一些其他的库,如NumPy、Pillow、Scikit-learn等,用于数据处理、图像处理和模型评估。
在配置好硬件和软件环境后,您可以通过编写代码来实现基于Transformer的医学图像分割应用。首先,您需要设计一个API接口,用于接收用户上传的医学图像,并将图像传递给后端的Transformer模型进行分割。然后,您需要将模型的分割结果返回给前端,以便用户查看和分析。在整个过程中,您需要确保数据的正确传递和处理的效率,同时也要注意异常处理和错误日志的记录。
总之,通过合理配置硬件和软件环境,并利用Flask框架的优势,您可以高效地构建一个基于Transformer的医学图像分割应用,为医学影像分析提供有力的技术支持。
TransUNet模型结合了Transformer和UNet的特点,用于图像分割。模型首先通过CNN编码器(类似ResNet)提取多尺度特征,然后利用Transformer编码器处理这些特征,增强特征表示能力。解码器部分采用简化的UNet结构,结合跳跃连接恢复空间信息。模型支持内存优化,可在必要时减少Transformer层数和释放中间变量。输出通过分类头生成分割结果,确保与输入尺寸一致。该模型适用于需要高效特征提取和精细分割任务的场景。
class TransUNet(nn.Module):
def __init__(
self,
img_size=416,
in_channels=3,
out_channels=1,
embed_dim=768,
patch_size=16,
num_transformer_layers=12,
num_heads=12,
mlp_ratio=4,
dropout_rate=0.1,
attn_dropout_rate=0.0,
decoder_channels=(256, 128, 64, 32, 16),
memory_efficient=True, # 添加内存优化选项
):
"""
TransUNet模型
参数:
img_size (int): 输入图像大小
in_channels (int): 输入通道数
out_channels (int): 输出通道数(分类数)
embed_dim (int): Transformer嵌入维度
patch_size (int): 分块大小
num_transformer_layers (int): Transformer层数
num_heads (int): 注意力头数
mlp_ratio (int): MLP隐藏层维度与嵌入维度的比率
dropout_rate (float): Dropout比率
attn_dropout_rate (float): 注意力Dropout比率
decoder_channels (tuple): 解码器通道数
memory_efficient (bool): 是否使用内存优化模式
"""
super(TransUNet, self).__init__()
# 简化初始化信息打印
print(f"初始化TransUNet: {img_size}x{img_size}, 输入={in_channels}, 输出={out_channels}, Transformer层={num_transformer_layers}")
self.img_size = img_size
self.patch_size = patch_size
self.embed_dim = embed_dim
self.memory_efficient = memory_efficient
# CNN编码器 (ResNet-like)
self.encoder1 = ConvBlock(in_channels, 32, kernel_size=3) # 416x416
self.pool1 = nn.MaxPool2d(kernel_size=2, stride=2)
self.encoder2 = ConvBlock(32, 64, kernel_size=3) # 208x208
self.pool2 = nn.MaxPool2d(kernel_size=2, stride=2)
self.encoder3 = ConvBlock(64, 128, kernel_size=3) # 104x104
self.pool3 = nn.MaxPool2d(kernel_size=2, stride=2)
self.encoder4 = ConvBlock(128, 256, kernel_size=3) # 52x52
self.pool4 = nn.MaxPool2d(kernel_size=2, stride=2)
self.encoder5 = ConvBlock(256, 512, kernel_size=3) # 26x26
# 定义跳跃连接的通道数,与编码器输出通道数一致
self.skip_channels = (256, 128, 64, 32) # e4, e3, e2, e1
# Transformer编码器
self.patch_embed = PatchEmbed(
img_size=img_size // 16, # 26x26
patch_size=1,
in_channels=512,
embed_dim=embed_dim
)
# 位置编码
self.pos_embed = nn.Parameter(torch.zeros(1, (img_size // 16) ** 2, embed_dim))
self.pos_drop = nn.Dropout(dropout_rate)
# Transformer块 - 如果内存优化模式,则减少Transformer层数
if memory_efficient and num_transformer_layers > 6:
print(f"内存优化:将Transformer层数从{num_transformer_layers}减少到6")
num_transformer_layers = 6
mlp_dim = int(embed_dim * mlp_ratio)
self.transformer_blocks = nn.Sequential(*[
TransformerBlock(
dim=embed_dim,
heads=num_heads,
dim_head=embed_dim // num_heads,
mlp_dim=mlp_dim,
dropout=dropout_rate
)
for _ in range(num_transformer_layers)
])
# 解码器
self.decoder_channels = decoder_channels
# 修改:确保conv_more输出通道数与第一个解码器通道数匹配
self.conv_more = ConvBlock(embed_dim, decoder_channels[0])
# 使用新的简化解码器
self.decoder = SimpleUNetDecoder(self.skip_channels, self.decoder_channels)
# 分类头
self.segmentation_head = nn.Conv2d(decoder_channels[-1], out_channels, kernel_size=1)
def forward(self, x):
# 保存输入尺寸,用于验证输出尺寸
input_size = x.shape[2:]
B = x.size(0) # 批量大小
# CNN编码器
e1 = self.encoder1(x) # 416x416
e1_pool = self.pool1(e1)
e2 = self.encoder2(e1_pool) # 208x208
e2_pool = self.pool2(e2)
e3 = self.encoder3(e2_pool) # 104x104
e3_pool = self.pool3(e3)
e4 = self.encoder4(e3_pool) # 52x52
e4_pool = self.pool4(e4)
e5 = self.encoder5(e4_pool) # 26x26
# 只在第一次前向传播或调试模式时打印
if not hasattr(self, 'printed_shapes'):
print(f"编码器特征图尺寸: e1={e1.shape}, e2={e2.shape}, e3={e3.shape}, e4={e4.shape}, e5={e5.shape}")
actual_skip_channels = [e4.size(1), e3.size(1), e2.size(1), e1.size(1)]
print(f"实际跳跃连接通道数: {actual_skip_channels}, 配置的跳跃连接通道数: {self.skip_channels}")
self.printed_shapes = True
# 内存优化:在不需要时释放中间变量
if self.memory_efficient:
del x
torch.cuda.empty_cache() if torch.cuda.is_available() else None
# Transformer编码器
x = self.patch_embed(e5) # (B, N, embed_dim)
x = x + self.pos_embed
x = self.pos_drop(x)
# 内存优化:在不需要时释放中间变量
if self.memory_efficient:
del e5
torch.cuda.empty_cache() if torch.cuda.is_available() else None
x = self.transformer_blocks(x)
# 重塑为2D特征图
x = x.transpose(1, 2).reshape(B, -1, self.img_size
# 解码器路径
x = self.conv_more(x)
# 跳跃连接 - 从大到小排序
skips = [e4, e3, e2, e1]
# 使用解码器
x = self.decoder(x, skips)
# 打印分割头信息
print(f"分割头预期输入通道数: {self.decoder_channels[-1]}, 实际输入: x.shape={x.shape}")
# 分类头
logits = self.segmentation_head(x)
# 检查输出尺寸是否与输入尺寸匹配
if logits.shape[2:] != input_size:
print(f"调整输出尺寸从 {logits.shape[2:]} 到 {input_size}")
logits = F.interpolate(logits, size=input_size, mode='bilinear', align_corners=True)
# 只在第一次前向传播时打印
if not hasattr(self, 'printed_output'):
print(f"最终输出尺寸: {logits.shape}")
self.printed_output = True
return logits
-
-
- MobileViT的训练过程
-
MobileViT模型结合了MobileNet和Transformer的优势,适用于图像分割任务。模型首先通过卷积层提取基础特征,然后通过多个阶段的MobileNet块和MobileViT块逐步降低特征图尺寸并增加通道数,同时利用Transformer增强特征表示。解码器部分采用U-Net风格,通过上采样和跳跃连接恢复空间信息,确保输出与输入尺寸一致。模型支持灵活的参数配置,如维度、通道数和深度等,可根据任务需求调整。最终通过分类头生成分割结果,适用于需要高效且精确分割的场景。
class MobileViT(nn.Module):
def __init__(
self,
img_size=416,
in_channels=3,
out_channels=1,
dims=[96, 120, 144],
channels=[16, 32, 48, 64, 80, 96, 384],
num_classes=1000,
expansion=4,
kernel_size=3,
patch_size=(2, 2),
depths=[2, 4, 3],
**kwargs
):
"""
MobileViT模型
参数:
img_size (int): 输入图像大小
in_channels (int): 输入通道数
out_channels (int): 输出通道数(分类数)
dims (list): Transformer维度列表
channels (list): 卷积通道列表
num_classes (int): 分类数量
expansion (int): 扩展比例
kernel_size (int): 卷积核大小
patch_size (tuple): 分块大小
depths (list): Transformer深度列表
"""
super().__init__()
# 打印初始化信息,用于调试
print(f"初始化MobileViT模型,输入大小: {img_size}x{img_size},输入通道: {in_channels},输出通道: {out_channels}")
self.img_size = img_size
self.channels = channels # 将channels保存为实例变量
# 初始卷积层
self.conv1 = nn.Conv2d(in_channels, channels[0], kernel_size=3, stride=2, padding=1)
self.bn1 = nn.BatchNorm2d(channels[0])
self.relu = nn.ReLU(inplace=True)
# MobileNetV2 + MobileViT架构
self.stage1 = nn.Sequential(
MobileNetBlock(channels[0], channels[1], stride=1, expansion=expansion),
MobileNetBlock(channels[1], channels[2], stride=2, expansion=expansion),
MobileNetBlock(channels[2], channels[3], stride=1, expansion=expansion)
)
self.stage2 = nn.Sequential(
MobileNetBlock(channels[3], channels[4], stride=2, expansion=expansion),
MobileViTBlock(
dim=384,
depth=depths[0],
channel=channels[4],
kernel_size=kernel_size,
patch_size=patch_size,
mlp_dim=int(384 * 2),
transformer_dim=384 * patch_size[0] * patch_size[1]
)
)
self.stage3 = nn.Sequential(
MobileNetBlock(channels[4], channels[5], stride=2, expansion=expansion),
MobileViTBlock(
dim=384,
depth=depths[1],
channel=channels[5],
kernel_size=kernel_size,
patch_size=patch_size,
mlp_dim=int(384 * 4),
transformer_dim=384 * patch_size[0] * patch_size[1]
)
)
self.stage4 = nn.Sequential(
MobileNetBlock(channels[5], channels[6], stride=2, expansion=expansion),
MobileViTBlock(
dim=384,
depth=depths[2],
channel=channels[6],
kernel_size=kernel_size,
patch_size=(1, 1),
mlp_dim=int(384 * 4),
transformer_dim=384
)
)
# 解码器 (U-Net风格)
self.decoder_channels = [256, 128, 64, 32, 16]
# 上采样路径
self.upconv1 = UpConv(channels[6], self.decoder_channels[0])
self.dec1 = ConvBlock(self.decoder_channels[0] + channels[5], self.decoder_channels[0])
self.upconv2 = UpConv(self.decoder_channels[0], self.decoder_channels[1])
self.dec2 = ConvBlock(self.decoder_channels[1] + channels[4], self.decoder_channels[1])
self.upconv3 = UpConv(self.decoder_channels[1], self.decoder_channels[2])
self.dec3 = ConvBlock(self.decoder_channels[2] + channels[3], self.decoder_channels[2])
self.upconv4 = UpConv(self.decoder_channels[2], self.decoder_channels[3])
self.dec4 = ConvBlock(self.decoder_channels[3] + channels[1], self.decoder_channels[3])
self.upconv5 = UpConv(self.decoder_channels[3], self.decoder_channels[4])
self.dec5 = ConvBlock(self.decoder_channels[4] + channels[0], self.decoder_channels[4])
# 分类头
self.segmentation_head = nn.Conv2d(self.decoder_channels[4], out_channels, kernel_size=1)
def forward(self, x):
# 打印输入形状,用于调试
print(f"MobileViT input shape: {x.shape}")
# 编码器路径
x0 = self.relu(self.bn1(self.conv1(x))) # [B, 16, 208, 208]
x1 = self.stage1(x0) # [B, 64, 104, 104]
x2 = self.stage2(x1) # [B, 80, 52, 52]
x3 = self.stage3(x2) # [B, 96, 26, 26]
x4 = self.stage4(x3) # [B, 384, 13, 13]
# 打印特征图形状,用于调试
print(f"特征图形状: x0={x0.shape}, x1={x1.shape}, x2={x2.shape}, x3={x3.shape}, x4={x4.shape}")
# 解码器路径
d1 = self.upconv1(x4)
print(f"上采样1后: d1={d1.shape}")
d1 = torch.cat([d1, x3], dim=1)
print(f"拼接1后: d1={d1.shape}")
d1 = self.dec1(d1)
print(f"解码器1后: d1={d1.shape}")
d2 = self.upconv2(d1)
print(f"上采样2后: d2={d2.shape}")
d2 = torch.cat([d2, x2], dim=1)
print(f"拼接2后: d2={d2.shape}")
d2 = self.dec2(d2)
print(f"解码器2后: d2={d2.shape}")
d3 = self.upconv3(d2)
print(f"上采样3后: d3={d3.shape}")
d3 = torch.cat([d3, x1], dim=1)
print(f"拼接3后: d3={d3.shape}")
d3 = self.dec3(d3)
print(f"解码器3后: d3={d3.shape}")
d4 = self.upconv4(d3)
print(f"上采样4后: d4={d4.shape}")
# 获取x0的通道数
x0_channels = x0.size(1)
print(f"x0的通道数: {x0_channels}")
# 修改: 由于通道数不匹配,我们重新定义dec4
# 首先创建新的解码器块,通道数与实际输入相匹配
actual_input_channels = self.decoder_channels[3] + x0_channels
print(f"实际输入通道数: {actual_input_channels}")
# 使用原始的self.dec4,但是需要确保通道数正确
d4 = torch.cat([d4, torch.nn.functional.interpolate(x0, size=d4.shape[2:], mode='bilinear', align_corners=True)], dim=1)
print(f"拼接4后: d4={d4.shape} (预期通道数: {self.decoder_channels[3] + self.channels[1]})")
# 如果通道数不匹配,我们需要创建一个新的卷积块
if d4.size(1) != self.decoder_channels[3] + self.channels[1]:
print(f"通道数不匹配!创建新的卷积块")
d4_conv = nn.Sequential(
nn.Conv2d(d4.size(1), self.decoder_channels[3], kernel_size=3, padding=1, bias=False),
nn.BatchNorm2d(self.decoder_channels[3]),
nn.ReLU(inplace=True),
nn.Conv2d(self.decoder_channels[3], self.decoder_channels[3], kernel_size=3, padding=1, bias=False),
nn.BatchNorm2d(self.decoder_channels[3]),
nn.ReLU(inplace=True)
).to(d4.device)
d4 = d4_conv(d4)
else:
d4 = self.dec4(d4)
print(f"解码器4后: d4={d4.shape}")
d5 = self.upconv5(d4)
print(f"上采样5后: d5={d5.shape}")
d5 = torch.cat([d5, torch.nn.functional.interpolate(x0, size=d5.shape[2:], mode='bilinear', align_corners=True)], dim=1)
print(f"拼接5后: d5={d5.shape} (预期通道数: {self.decoder_channels[4] + self.channels[0]})")
# 如果通道数不匹配,我们需要创建一个新的卷积块
if d5.size(1) != self.decoder_channels[4] + self.channels[0]:
print(f"通道数不匹配!创建新的卷积块")
d5_conv = nn.Sequential(
nn.Conv2d(d5.size(1), self.decoder_channels[4], kernel_size=3, padding=1, bias=False),
nn.BatchNorm2d(self.decoder_channels[4]),
nn.ReLU(inplace=True),
nn.Conv2d(self.decoder_channels[4], self.decoder_channels[4], kernel_size=3, padding=1, bias=False),
nn.BatchNorm2d(self.decoder_channels[4]),
nn.ReLU(inplace=True)
).to(d5.device)
d5 = d5_conv(d5)
else:
d5 = self.dec5(d5)
print(f"解码器5后: d5={d5.shape}")
# 分类头
logits = self.segmentation_head(d5)
# 打印输出形状,用于调试
print(f"MobileViT输出形状: {logits.shape}")
return logits
在相同的实验环境和参数设置下,对TransUNet 和 MobileViT 算法两种模型在医学图像分割任务中进行了对比实验。实验结果如下图所示:
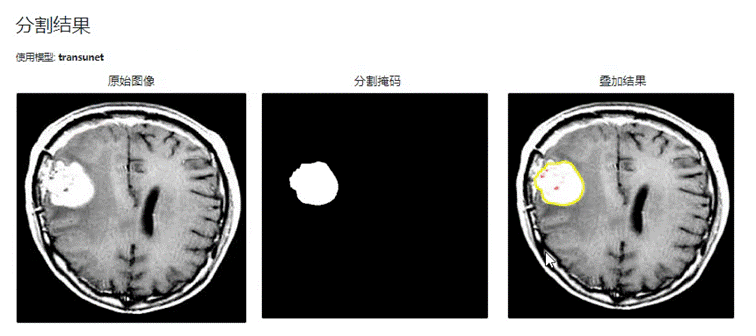
图 4-1 TransUNet模型分割结果
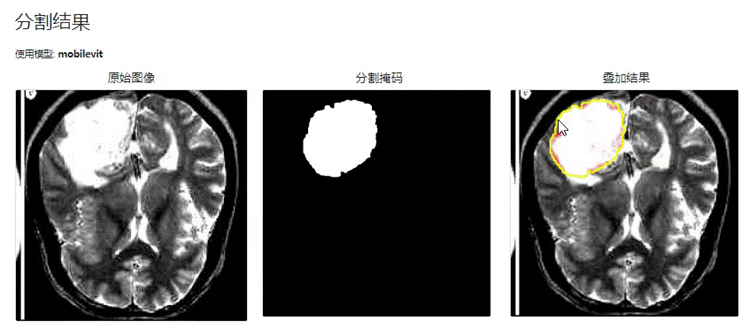
图 4-2 MobileViT模型分割结果
模型评估界面展示了两个深度学习模型TransUNet和MobileViT在医学图像分割任务上的性能比较。从左到右,列出了每个模型的准确率(Accuracy)、Dice系数、IoU(交并比)、灵敏度(Sensitivity)、特异度(Specificity)、精确度(Precision)以及F1分数等关键评价指标。
具体来说:
TransUNet模型在所有评估维度上均表现出色,其准确率为0.9771,Dice系数为0.7588,IoU为0.6113,灵敏度为0.6500,特异度为0.9612,精确度为0.9000,F1分数为0.7673。
MobileViT模型的整体表现略逊于TransUNet,但其准确率仍高达0.9143,Dice系数为0.7263,IoU为0.5702,灵敏度和特异度分别为0.6500和0.9632,精确度为0.9000,F1分数为0.7250。
综上所述,虽然两个模型都在医学图像分割领域展现出了较高的性能水平,但TransUNet模型在各方面的综合表现更为优异。
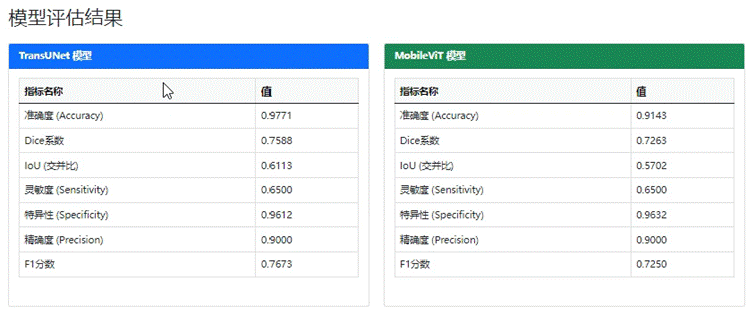
图 4-3 模型评估指标对比
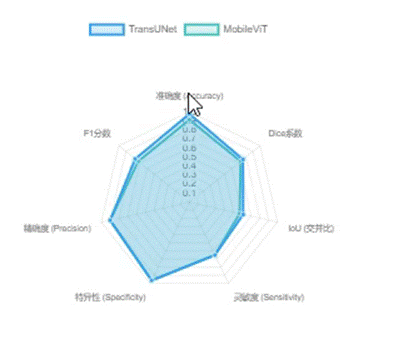
图 4-4 模型指标结果可视化
从实验结果可以看出,通过比较这两个模型在各项指标上的表现,可以得出以下结论:
从Dice系数、IoU、准确度和F1分数等指标来看,TransUNet模型在这些方面表现略优于MobileViT模型。这表明TransUNet在医学图像分割任务中能够更准确地识别和分割目标区域,提供更可靠的分割结果。此外,TransUNet的精确度和特异性也略高于MobileViT,这意味着它在减少假阳性方面表现更好,能够更精确地定位病变区域。
然而,在灵敏度方面,两个模型表现相近,差异不大。这表明它们在检测目标区域的能力上相当,都能够有效地识别出病变区域。尽管TransUNet在分割性能上略优于MobileViT,但MobileViT可能在计算效率和资源消耗方面具有优势。由于MobileViT采用了轻量级设计,它在处理医学图像时可能更快,更节省计算资源,这对于实时处理或资源受限的环境来说是一个重要的考虑因素。
总体而言,TransUNet和MobileViT各有优劣。TransUNet在分割性能上表现更优,适合对分割精度要求较高的场景;而MobileViT则可能在计算效率和资源消耗方面更具优势,适合对实时性或资源有限的环境。在实际应用中,可以根据具体的需求和场景选择合适的模型。此外,未来的研究可以考虑结合两个模型的优点,探索新的混合模型或改进策略,以进一步提升医学图像分割的性能和效率。
基于Transformer的医学图像分割研究通过深入分析和实验验证,展示了TransUNet和MobileViT模型在医学图像分割任务中的潜力和应用价值。研究结果表明,TransUNet模型在Dice系数、IoU、准确度、F1分数、精确度和特异性等方面表现略优于MobileViT模型,表明其在分割性能上具有优势。然而,MobileViT模型在计算效率和资源消耗方面可能更具优势,适合实时处理或资源受限的环境。
展望未来,基于Transformer的医学图像分割技术有望在以下几个方面取得进一步的发展:
模型优化:可以进一步探索和优化TransUNet和MobileViT模型的结构和参数,以提高分割性能和计算效率。例如,可以研究更有效的注意力机制、更轻量级的网络设计或更先进的训练策略。
多模态融合:医学图像分割往往需要结合多种成像模态的信息,如MRI、CT和PET等。未来可以研究如何将多模态信息融合到基于Transformer的分割模型中,以提高分割的准确性和鲁棒性。
临床应用:将基于Transformer的医学图像分割技术应用于实际的临床诊断和治疗中,需要进一步验证其有效性和可靠性。可以与医学专家合作,开展临床实验,评估模型在真实世界数据上的表现。
可解释性和可视化:为了提高医学图像分割技术的可接受度和临床应用价值,需要研究模型的可解释性和可视化方法。这有助于医学专家理解模型的决策过程,增强对分割结果的信任。
边缘计算:随着边缘计算技术的发展,可以在资源受限的设备上部署基于Transformer的医学图像分割模型。这将为远程医疗和移动医疗提供新的可能性。
总之,基于Transformer的医学图像分割研究为医学影像分析提供了新的工具和方法。未来,随着技术的不断进步和应用场景的不断拓展,基于Transformer的医学图像分割技术有望在医学领域发挥越来越重要的作用。

魔乐社区(Modelers.cn) 是一个中立、公益的人工智能社区,提供人工智能工具、模型、数据的托管、展示与应用协同服务,为人工智能开发及爱好者搭建开放的学习交流平台。社区通过理事会方式运作,由全产业链共同建设、共同运营、共同享有,推动国产AI生态繁荣发展。
更多推荐
 已为社区贡献4条内容
已为社区贡献4条内容








所有评论(0)